JIPB | 福建农林大学顾连峰团队开发表观多组学整合分析与可视化工具

在表观遗传学研究中, 染色质可及性、组蛋白修饰、DNA甲基化以及RNA修饰等调控层协同塑造了基因表达状态。ChIP-seq、ATAC-seq、BS-seq和m6A-seq等技术能够从多个层面系统揭示基因调控网络。然而, 不同组学数据之间分析逻辑差异大、输入格式复杂、结果展示分散, 如何将异构数据进行高效整合分析, 并进一步输出可解释的图形结果, 成为多组学分析中较为迫切的需求。
近日, 福建农林大学顾连峰团队在JIPB发表了题为“OmicsCanvas: A multi-omics platform for integration and visualization of epigenetic regulation”的研究论文 (https://doi.org/10.1111/jipb.70258)。该研究针对多组学整合分析中的实际需求, 开发了一个兼具关联分析能力与图形绘制功能的一体化软件流程。
表观遗传学的检测技术得益于不同组学文库的深度挖掘, ATAC-seq和ChIP-seq展示染色质状态与组蛋白修饰, BS-seq揭示DNA甲基化图谱, 而m6A-seq则关注RNA修饰层面的动态变化, RNA-seq反映基因表达水平。若能将不同类型的组学数据纳入同一分析框架中进行关联分析, 将有助于完整理解基因表达与表观调控之间的关联。为此研究团队开发了多组学关联分析工具, 该工具以组学联配文件BAM和基因注释文件GFF/BED为标准输入, 将多组学信号映射到统一的坐标体系中, 在一致的分析框架下实现跨组学信号的量化、归一化、聚类以及可视化输出。该流程核心优势在于“统一”, 不同来源的组学数据可以被投射到统一坐标系中进行处理, 并且支持表观组学数据的联合分析与模式聚类识别。
在图形展示方面, 该工具输出多种结果形式, 包括表观信号的全基因组metaplot、DNA甲基化分布图、单基因环形wiggle图以及线性wiggle图等。值得一提的是, 该工具特别支持用户指定基因集的表达和修饰关联热图, 包括组蛋白修饰与表达的关联热图、DNA甲基化与表达的关联热图以及染色质可及性与基因表达的关联热图等, 便于研究者从表达分层的角度深入解析表观调控特征 (图1)。
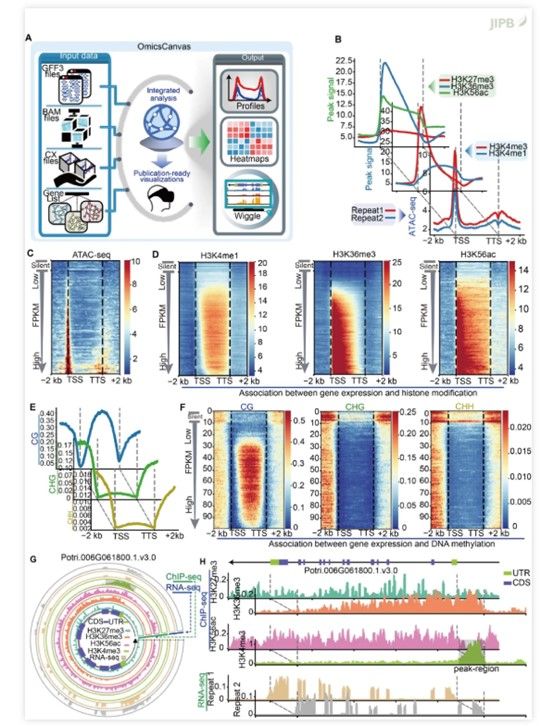
图1 表观遗传组关联分析整合及可视化
该软件流程可在Linux环境中进行批量分析。此外, 研究团队还基于Python/PySide6 (Qt) 开发了图形用户界面 (GUI), 将原有命令行脚本组织为模块化流程, 支持在Windows与Linux桌面环境中部署。这一设计使该流程不仅适用于具有编程基础的用户, 也便利了希望通过图形界面开展分析的研究者。该工具为表观组与转录组联合研究提供了一个可复用、可扩展且可直接服务于生物学解析的高效绘图工具。
福建农林大学林学院博士生张泽宇为该论文第一作者, 福建农林大学顾连峰教授为通讯作者。该研究得到国家重点研发计划、国家自然科学基金、福建省自然科学基金以及福建农林大学高峰学科支持。
文章引用:Zhang, Z., Ma, Z., Hua, T., Liu, X., Xiang, S., Gu, L. (2026). OmicsCanvas: A multi-omics platform for integration and visualization of epigenetic regulation. J. Integr. Plant Biol. https://doi.org/10.1111/jipb.70258











